INTRODUCCIÓN
Klebsiella pneumoniae carbapenemasa (KPC) se identificó originalmente en los EE.UU. en 1996. Desde entonces, se han expandido a nivel internacional entre las bacterias Gram negativas, especialmente en K. pneumoniae, aunque su epidemiología es diversa en todos los países y regiones. La mortalidad en los pacientes infectados con organismos positivos para KPC es alta, tal vez como resultado de las opciones terapéuticas limitadas (a menudo colistina, tigeciclina, o aminoglucósidos) 1,2.
Argentina reportó los primeros casos en el año 2006, en cepas de una K. pneumoniae y C. freundii aisladas de colección abdominal de una paciente transplantada 3).
En Paraguay, los primeros aislamientos de cepas portadoras de carbapenemasa tipo KPC aparecieron en setiembre del año 2.009, en cepas de K. pneumoniae y E. cloacae, simultáneamente en 2 centros hospitalarios de Asunción, la capital del país4.
A partir de esos aislamientos, fueron detectados en otros centros asistenciales, incluyendo el interior del país. Además fue confirmada la presencia de la enzima en varias otras especies de enterobacterias, siendo K. pneumoniae la prevalente entre todas ellas; sin embargo, ninguna en Salmonella spp., en el que es poco frecuente5,6,7,8. En cuanto a las cepas de Salmonella spp., la Sección Enteropatógenos del Laboratorio Central de Salud Pública confirmó en el año 2.014 que de las 73 cepas remitidas para estudios de serotipificación, solo el 8% correspondieron al serotipo Javiana, siendo Typhimurium el prevalente (33%). Este es reporte del primer caso de hallazgo de esta enzima en el género Salmonella en nuestro país, aislada de una paciente pediátrica, y uno de los pocos reportados en la región. Además, fueron aislados en muestras de la misma paciente otros gérmenes multirresistentes.
DESCRIPCION DEL CASO
La cepa de Salmonella aislada, provino de una paciente de sexo femenino, de 1 año 4 meses de edad, quien ingresó a la unidad de cuidados intensivos (UCI) de un centro hospitalario de Asunción, Paraguay, por cuadro de insuficiencia respiratoria aguda, remitida desde un hospital de Ciudad del Este, distante a 325 km, donde estuvo hospitalizada 14 días. La paciente además presentaba al ingreso cuadro de desnutrición proteico-calórica (Marasmo-Kwashiorkor). Estudios laboratoriales para VIH y RK 39 resultaron negativos. En el Hospital de Ciudad del Este fue aislada K. pneumoniae portadora de beta-lactamasa de espectro extendido a partir de una muestra del aparato respiratorio. Posteriormente, ya internada en UCI fueron aislados otros gérmenes multirresistentes de diferentes muestras clínicas: Enterococo Vancomicina Resistente a partir de heces y K. pneumoniae multiresistente de una muestra de punción pulmonar; la cual fue remitida al Laboratorio Central de Salud Pública, laboratorio de referencia nacional, para estudios de portación de mecanismos de resistencia. También, a partir de una muestra de heces, se aisló Salmonella sp., y ante la observación de halos reducidos frente a carbapenemes por el método de difusión de Kirby Bauer9 la cepa fue remitida al laboratorio de referencia nacional.
RESULTADOS
Tipificación: La cepa de Salmonella sp. fue identificada por pruebas bioquímicas utilizando el Manual de Procedimientos del Servicio de Enteropatógenos del Laboratorio de Referencia10 y los estudios de serotipificación se realizaron con antisueros específicos Denka-Seiken®11) que confirmaron a la cepa como serotipo Javiana. Sensibilidad: Los estudios de sensibilidad fueron realizados por los métodos de difusión de discos (Kirby Bauer), Concentración Inhibitoria Mínima por el método epsilométrico (E-test®)9) y con el equipo automatizado (VITEK-2 Compact®). Tabla 1.
Tabla 1 Susceptibilidad antimicrobiana de Salmonella Javiana portadora de carbapenemasa, aislada de la paciente internada en UCI
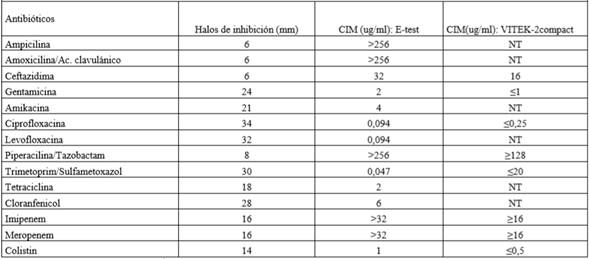
NT: No testado
Estudios fenotípicos: Las pruebas fenotípicas realizadas a ambas cepas fueron: Test de Hogde modificado (Foto 1) siguiendo pautas del CLSI 9, BLUE CARBA-método colorimétrico para detección rápida de carbapenemasas 12,13,14,15 siendo ambos resultados positivos y el método de inactivación del carbapenem 16 arrojó 6 mm de diámetro para el meropenem.
Además se llevaron a cabo las pruebas de sinergia, utilizando los discos de ethylen diamino tetra acético (EDTA) para la detección de carbapenemasas del tipo metalo-beta-lactamasa (MBL) y de ácido fenil borónico (PBA) para carbapenemasas clase A, obteniendo resultado positivo solo para la prueba con el PBA (Foto 2), sugiriendo la presencia de carbapenemasa de clase A en ambas cepas.
Estudios genotípicos: La reacción en cadena de la polimerasa (PCR) evidenció la presencia del gen que codifica para la enzima carbapenemasa KPC. El protocolo de amplificación utilizado: desnaturalización inicial a 94°C por 5 min, 30 ciclos de desnaturalización a 94°C por 30 seg, annealing a 50°C por 30 seg y extensión a 72°C por 1 min, y extensión final a 72°C por 10 min17 (termociclador THERMO Electrón Corporation (PXE 0.5 Thermal Cycler). Los productos de la amplificación separamos por electroforesis en gel de agarosa 2%, en buffer TAE 0,5 X y teñidos con bromuro de etidio al 1% para una observación posterior con luz UV con el equipo BIORAD UV Transilluminator 2000.
Los cebadores (premiers) utilizados para la detección molecular (PCR) de mecanismos de resistencia antimicrobiana se detallan en la Tabla 2.
Estudios de relación genética: La subtipifacion molecular se realizo por electroforesis en gel de campo pulsado (PFGE) con equipo CHEFF DR III-BioRad, enzima de restricción Xbal (Promega, EEUU), cepa estándar CDC-H98-12 (Salmonella Braenderup), de acuerdo al protocolo estandarizado de Pulse Net internacional para Salmonella18,19 el análisis del patrón de restricción obtenido se realizó con el software Gelcompare II versión 5.1, el cual mostró que el aislamiento posee un patron único Xbal de Salmonella Javaiana diferente a todos los patrones presentes actualmente en la Base de Datos Nacional. (Figura 1)

Figura 1 Dendograma de relación genética correspondiente a patrones únicos de Salmonella Javiana presentes en Base de Datos Nacional (BDN)
Estudios de secuenciación: El estudio de secuenciación fue realizado por Macrogen, y los resultados fueron analizados por National Center for Biotechnology Information (NCBI BLAST). Para ello fue utilizada la secuencia de blaKPC genérica. El resultado obtenido revela una identidad del 100% con la variante KPC-2 (Klebsiella pneumoniae ssp.pneumoniae HS11286 plashmid pKPHS2, que contiene el gen de la carbapenemasa bla KPC-220
Otros resultados: La cepa K. pneumoniae aislada de la punción pulmonar de la misma paciente resulto ser portadora de varios genes de resistencia: CTX-M2, Qnr B, aac(6)-Ib-cr, KPC-2 (este ultimo sometido también a estudio de secuenciación) y Concentracion Inhibitoria Minima para colistin 12ug/ml.
Referencia de las cepas: Macrogen: Orden número 151210FN-007
DISCUSIÓN Y CONCLUSIÓN
Publicaciones hechas en la región revelan que cepas de Salmonella spp. portadoras de KPC son extremadamente raras5,6,7, siendo este aislamiento en el año 2015 el primero y el único, hasta la fecha reportado en Paraguay.
Este hallazgo, además de confirmar la portación del gen que codifica para la carbapenemasa por cepa de Salmonella entérica, revela que el mismo ocurre en un serotipo poco frecuente (8% en el año 2014), e incluso analizando los patrones genéticos de los aislados en el país, se vio la no relación clonal entre los mismos.
Los estudios de secuenciación han revelado que la secuencia de la enzima tiene 100% de similitud con la variante KPC-2, lo cual confirma la circulación de dicha variante en Paraguay.
Además, la recuperación de K. pneumoniae portadora de carbapenemasa tipo KPC (100% de similitud con la variable KPC-2) evidencia la diseminación de este mecanismo de resistencia entre las enterobacterias, y sugiere el traspaso de plásmido de una bacteria a la otra.
Es fundamental que los diferentes centros de atención lleven a cabo la vigilancia para la detección temprana de la aparición de estos mecanismos de resistencia, y notificar en caso de detección para que se tomen las medidas de aislamiento, puesto que diseminación se lleva a cabo sin discriminar género bacteriano.