Servicios Personalizados
Revista
Articulo
Indicadores
-
 Citado por SciELO
Citado por SciELO
Links relacionados
-
 Similares en
SciELO
Similares en
SciELO
Compartir
Memorias del Instituto de Investigaciones en Ciencias de la Salud
versión On-line ISSN 1812-9528
Mem. Inst. Investig. Cienc. Salud v.10 n.1 Asunción jun. 2012
ARTICULO ORIGINAL
PCR múltiple para la detección simultánea de los genes mecA y pvl en Staphylococcus spp
Multiplex PCR for simultaneous detection of mecA and pvl genes in Staphylococcus spp
Carpinelli Acevedo MLI, *Guillén Fretes RMII, Fariña NJI Basualdo WIII Aquino RIII
IDepartamento de Análisis Clínicos y Microbiología, Instituto de Investigaciones en Ciencias de la Salud-Universidad Nacional de Asunción. Paraguay
IIDepartamento de Biología Molecular y Genética, Instituto de Investigaciones en Ciencias de la Salud-Universidad Nacional de Asunción. Paraguay
IIIDepartamento de Epidemiología y Control de infecciones. Hospital General Pediátrico Niños de Acosta Ñú. Ministerio de Salud Pública y Bienestar Social. San Lorenzo-Paraguay
RESUMEN
Este estudio observacional descriptivo de corte transverso tuvo por objetivo estandarizar una PCR múltiple para la detección simultánea de los genes mecA y pvl en Staphylococcus spp. Se emplearon como cepas control: S. aureus ATCC 25923, S. aureus ATCC 43300 y un aislado de S. aureus portador de los genes mecA y pvl. La extracción de ADN se realizó por el método de ebullición. El límite de detección se estableció por medio de diluciones seriadas de ADN. Se determinó la aplicabilidad de la PCR múltiple testando 41 aislados de S. aureus y 51 Estafilococos coagulasa negativo (ECN) previamente caracterizados por métodos fenotípicos en noviembre del año 2009. Los productos de PCR fueron visualizados por electroforesis en gel de agarosa al 2% previa tinción con bromuro de etidio. Los productos de amplificación de la PCR múltiple presentaron tamaño esperado de 533pb y 433pb para los genes mecA y pvl respectivamente, con límites de detección de hasta 0,5 ng/µL. El gen mecA se detectó en 13 (31,7%) aislados de S. aureus y en 29 (56,7%) ECN. El gen pvl se detectó en 2 (4,9%) S. aureus y no fue detectado en ECN. La presencia del gen mecA tuvo 100% de concordancia con los métodos fenotípicos. Esta técnica es una herramienta útil en la confirmación de cepas de Estafilococos meticilino resistentes e identificación del gen pvl, además de ser relativamente sencilla con la ventaja de detectar ambos genes en una sola reacción.
Palabras claves: Staphylococcus aureus, Estafilococos coagulasa negativos, meticilino resistencia, gen mecA, gen pvl.
ABSTRACT
The aim of this cross sectional observational study was to standardize a multiplex PCR for simultaneous detection of mecA and pvl genes in Staphylococcus spp. S. aureus strains ATCC 25923 and S.aureus ATCC 43300 were used as controls as well as an isolate of S. aureus carrying mecA and pvl genes. The boiling method was performed for DNA extraction and the detection limit was established by serial dilutions of DNA. We determined the applicability of the multiplex PCR by testing 41 isolates of S. aureus and 51 coagulase negative staphylococci (CNS) previously characterized by phenotypic methods in november 2009. The PCR products were visualized by agarose gel electrophoresis in 2% after ethidium bromide staining. The size of the amplified products of the multiplex PCR corresponded to those expected, 433bp for mecA and 533bp for pvl, with detection limits up to 0.5 ng/µL. The mecA gene was detected in 13 (31.7%) isolates of S. aureus and 29 (56.7%) CNS. The pvl gene was detected in 2 (4.9%) isolates of S. aureus and was not detected in CNS. A 100% concordance was obtained between the presence of mecA and phenotypic methods. This technique is a useful tool in the confirmation of methicillin-resistant Staphylococcus strains and identification of the pvl gene, in addition to being relatively simple, with the advantage of detecting both genes in a single reaction.
Keywords: Staphylococcus aureus, coagulase negative staphylococci, methicillin, resistance, mecA, pvl.
INTRODUCCIÓN
Las enfermedades infecciosas constituyen una de las primeras causas de morbilidad y mortalidad a nivel mundial y Staphylococcus aureus es una de las especies más comúnmente implicadas en estas infecciones (1). Así mismo, otros microorganismos del género Staphylococcus son de gran transcendencia clínica como algunas especies de estafilococos coagulasa negativa (ECN), Enterococcus y Streptococcus (2).
Uno de los principales desafíos que enfrentan hoy en día los sistemas de salud a nivel mundial, es el gran aumento de la resistencia a los antimicrobianos. El género estafilococo, principalmente S. aureus, ha desarrollado resistencia a prácticamente todas las familias de antibióticos (1). Las primeras cepas de S. aureus resistentes a meticilina (SARM) surgen a partir de 1960, apenas unos años después de haber sido introducida como tratamiento(3). A partir de la aparición de estas primeras cepas, la resistencia a meticilina fue aumentado en gran manera en todo el mundo (1,4-7).
La resistencia a meticilina está codificada por el gen mecA, el cual codifica una proteína de unión a penicilina alterada, la PBP2a, de baja afinidad a los antibióticos betalactámicos. Existen diferentes tipos de PBPs, éstas son responsables del proceso de transpeptidación durante la síntesis de la pared celular y son sitio blanco de acción de los antibióticos betalactámicos. Las bacterias que expresan la PBP2a pueden seguir sintetizando su pared celular aún en presencia de éstos antibióticos, por lo que la presencia del gen mecA confiere resistencia a todos los antibióticos betalactámicos sin excepción (1). El gen mecA se encuentra dentro del casete cromosómico estafilocóccico, elemento genético móvil que contiene: el complejo mec, el complejo ccr que codifica para recombinasas responsables de la movilidad, y regiones accesorias J–junkyard que son componentes no esenciales del casete, que pueden llevar determinantes adicionales de resistencia a antibióticos no betalactámicos (8,9).
Por mucho tiempo el SAMR fue considerado un germen exclusivamente nosocomial – (SAMR adquirido en los hospitales [SAMR-AH]), sin embargo en los últimos años éste germen ha emergido como causa importante de infecciones adquiridas en la comunidad, estas cepas se caracterizan, por la presencia de un factor de virulencia llamado leucocidina de Panton-Valentine (PVL), codificada por dos genes co-transcriptos lukS/F-PV que causa destrucción de leucocitos y necrosis tisular, generalmente producen infecciones de piel y partes blandas y los casos más graves están asociados a neumonías necrotizantes y sepsis (10,11).
La rápida y precisa detección de SAMR es importante para guiar una apropiada terapia antibiótica y evitar la diseminación nosocomial de éstas cepas. Errores en la detección de la meticilino resistencia tienen graves consecuencias, un resultado de falsa sensibilidad puede dar lugar a una falla de tratamiento, y un resultado de falsa resistencia implica un alto costo por tener al paciente aislado y por el uso innecesario de glucopéptidos, con el consecuente riesgo de selección de resistencia a éste antibiótico(12). El CLSI (Clinical and Laboratory Standards Institute), ha recomendado inicialmente para la detección fenotípica de la meticilino resistencia, el uso de discos de oxacilina, luego la utilización de discos de cefoxitina, introduciendo recientemente modificaciones en los puntos de corte; también recomiendan la prueba de aglutinación en látex para la detección de la proteína PBP2a o placas de agar Mueller-Hinton suplementado con NaCl al 4% como métodos alternativos para detectar la meticilino resistencia(13). La expresión fenotípica de la meticilino resistencia puede ser heterogénea e influenciada por las condiciones de cultivo como temperatura, tiempo de incubación, pH y contenido de NaCl del medio, entre otros, lo que dificulta su estandarización(14). La detección exacta y rápida de aislados meticilino resistentes actualmente constituye un desafío para los laboratorios y las técnicas moleculares de reacción en cadena de la polimerasa (PCR) se han convertido en una herramienta esencial.
Debido a la necesidad de contar en nuestro país de un método confirmatorio de la meticilino resistencia y poder detectar la presencia del factor de virulencia PVL, este trabajo tuvo por objetivo estandarizar una técnica de PCR múltiple para la detección simultánea de los genes mecA y pvl en Staphylococcus spp.
MATERIALES Y MÉTODOS
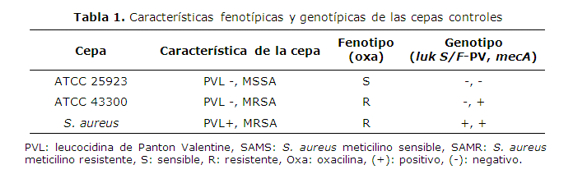
Cepas bacterianas: En este estudio observacional descriptivo de corte transverso fueron utilizados un total de 95 aislados de estafilococos incluyendo 3 cepas control de S. aureus (ATCC 25923, ATCC 43300 y S. aureus portador de los genes mecA y pvl, las características fenotípicas y genotípicas de estas cepas se describen en la tabla 1), 41 aislados de S. aureus obtenidos de trabajadores de la salud y 51 aislados clínicos de ECN, previamente caracterizados por métodos fenotípicos convencionales y remitidos al laboratorio de biología molecular en noviembre del año 2009.
Pruebas de identificación y de susceptibilidad a los antimicrobianos: La identificación de las especies se realizó por métodos microbiológicos convencionales(15,16). La resistencia a meticilina fue detectada por el método de difusión con discos utilizando discos de oxacilina (1 µg-Oxoid) y cefoxitina (30 µg-BioRad) siguiendo las recomendaciones del CLSI(13). En los aislados de ECN se detectó la presencia de la PBP2a por el método comercial de aglutinación (Oxoid).
Extracción de ADN: La extracción de ADN se realizó por el método de ebullición según lo describen Zhang y col con algunas modificaciones(17). Las colonias frescas de 24-48 horas fueron suspendidas en 400 µL de agua destilada estéril, llevadas a ebullición por 15 min y luego centrifugadas por 5 min a 15000 rpm. El sobrenadante conteniendo el ADN fue conservado a -20°C.
Amplificación por PCR: Los cebadores utilizados para la detección de los genes mecA y pvl fueron los descriptos previamente por Murakami y col.(18) y Lina y col.(19) respectivamente. En primer lugar se realizó la amplificación de regiones de los genes mecA y pvl en forma individual y luego se estandarizó la PCR múltiple para la detección simultánea de ambos genes. Las condiciones óptimas de la PCR múltiple se obtuvieron modificando las concentraciones de MgCl2, cebadores y condiciones de termociclado, siendo las óptimas las que se describen a continuación: buffer 1X (Fermentas, EU), dNTPs 0,4 mM (Bioline, UK), cebadores mecA-R, mecA-F, luk-PV-1 y luk-PV-2 0,5 µM (Genbiotech, AR), MgCl2 2,0 mM (Fermentas, EU), Taq polimerasa 1 U (Fermentas, EU) y agua tridestilada. Para la reacción de PCR se utilizó 2,5 µL de ADN molde obtenido por el método de ebullición en un volumen total de reacción de 25 µL. Se mantuvieron las condiciones de termociclado correspondiente al protocolo de Murakami y col.(18)
El límite de detección tanto de la PCR convencional como de la PCR múltiple se estableció por medio de diluciones seriadas de ADN de la cepa control portadora de los genes mecA y pvl, previa extracción con un kit comercial de purificación de ADN (Wizard-Promega®, USA), siguiendo las instrucciones del fabricante.
Los productos de PCR fueron visualizados mediante electroforesis en gel de agarosa al 2% (100V, 45 min). Los tamaños de bandas se verificaron corriendo en paralelo un marcador de peso molecular de 100 pb (Bioline, UK) y visualizados utilizando un transiluminador UV previa tinción con bromuro de etidio.
Para determinar la aplicabilidad de la PCR múltiple se analizaron 41 aislados de S. aureus obtenidos de trabajadores de la salud y 51 ECN aislados de muestras clínicas, previamente caracterizados por métodos fenotípicos convencionales (15,16).
Asuntos estadísticos: Los datos fueron introducidos y almacenados en una base de datos, utilizando una planilla electrónica, se utilizó la herramienta Microsoft Excel.
Asuntos éticos: El protocolo del estudio fue aceptado por el Comité Científico y Ético del Instituto de Investigaciones en Ciencias de la Salud. Se mantuvo la confidencialidad de los datos.
RESULTADOS
Previa a la estandarización de la técnica de PCR múltiple, se realizó la amplificación de ambos genes en forma individual utilizando las cepas controles que se detallan en la tabla 1. Los tamaños de los fragmentos obtenidos fueron de 533 pb para el gen mecA y 433 pb para el gen pvl (figura 1), con límites de detección de 0,5 ng/µL y 0,005 ng/µL respectivamente, lo que corresponde a aproximadamente 5x103 UFC/µL y 5x101 UFC/µL.
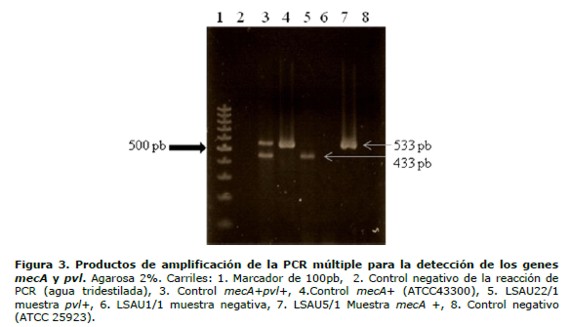
Utilizando como referencia los protocolos de Murakami y col. (18) y Lina y col. (19) se estandarizó una PCR múltiple para detectar ambos genes en una sola reacción. Para la estandarización se utilizó ADN de S. aureus portador de ambos genes (mecA y pvl), se probaron concentraciones de MgCl2 que fueron del rango de 1,0 mg/dL a 2,5 mg/dL, también se variaron las concentraciones de dNTPs y las condiciones de termociclado, quedando como óptimas aquellas que se detallan en materiales y métodos. Los productos de amplificación producidos por la PCR múltiple corresponden a los esperados (533 pb y 433 pb para los genes mecA y pvl respectivamente), la amplificación de ambos genes empleando la cepa de S. aureus ATCC 25923 utilizada como control negativo no generó producto de amplificación (figura 3). Para verificar si el uso de ambos cebadores en la PCR múltiple podría variar el límite de detección de alguno de los genes blanco de amplificación, se realizó la amplificación de diluciones seriadas de ADN de la cepa control de S. aureus portadora de ambos genes. Se encontró que en éstas condiciones, el límite de detección de ADN tanto para el gen mecA y el gen pvl fue de 0,5 ng/µL, que corresponde a aproximadamente 5x103 UFC/µL.
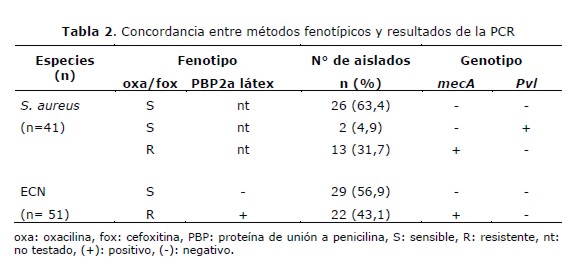
Para determinar la aplicabilidad de la PCR múltiple, se analizaron 41 aislados de S. aureus obtenidos de trabajadores de la salud y 51 ECN aislados de muestras clínicas. El gen mecA se detectó en 13 (31,7%) aislados de S. aureus y en 29 (56,7%) ECN. El gen pvl se detectó en 2 (4,9%) S. aureus y no fue detectado en ECN. Los resultados moleculares de detección del gen mecA tuvieron 100% de concordancia con los métodos fenotípicos de detección (tabla 2).
DISCUSIÓN
Debido al gran aumento que se ha producido en los últimos años en la resistencia a los antibióticos utilizados con mayor frecuencia en los tratamientos de las infecciones estafilocóccicas se requiere una detección precoz y eficaz de los mecanismos implicados, para así poder orientar e incluso modificar las estrategias terapéuticas (2).
Con este trabajo se logró implementar de forma eficiente y por primera vez en nuestro país, un sistema de PCR múltiple para la detección simultánea de los genes mecA y pvl, disminuyendo de esta manera el costo y tiempo utilizado que si se lo realiza de forma individual. Varios autores han desarrollado técnicas de PCR para la detección de estos genes que utilizan ensayos en forma separada o PCR múltiples con métodos comerciales de extracción, o técnicas de PCR en tiempo real, con lo que aumentan los costos y la complejidad de la técnica dificultando su aplicación en diversos laboratorios de nuestro país (18-20).
Nuestra técnica utiliza un método de extracción de ADN sumamente sencillo y práctico que no requiere la utilización de reactivos costosos ni tóxicos y puede ser realizada en un tiempo relativamente corto. Se han reportado diferentes métodos de extracción que requieren la utilización de enzimas líticas como lisostafina y solventes orgánicos como fenol-cloroformo (21,22). Perez-Roth y col. han reportado un método aun más práctico realizado a partir tan solo de una colonia, no encontrando diferencias con los otros métodos descritos (23).
La limitación de la técnica descrita en este trabajo se da con aquellos aislados en los que no se obtiene amplificación y que podrían ser causados por la presencia de inhibidores de la reacción de PCR. Mc CLure y col.(24), en el año 2006, desarrollaron una técnica de PCR múltiple para la detección simultánea de los genes mecA y pvl, este grupo de investigadores utilizaron como control interno la amplificación de una región del gen 16S rRNA. Así también, otros autores han utilizado otras secuencias blanco específicas para la identificación de S. aureus como los genes nuc y femB (23,25,26). Por este motivo queremos incluir un tercer gen a amplificar correspondiente a un control interno de estafilococos, que permitirá evaluar la calidad del ADN extraído y la presencia de inhibidores de amplificación.
Los métodos fenotípicos utilizados para la detección de la meticilino resistencia requiere de la expresión de la PBP2a, ésta puede ser heterogénea e influenciada por las condiciones de cultivo, por lo que es necesario contar con métodos confirmatorios como lo es la detección del gen mecA por la prueba de amplificación de ADN por PCR que es considerada el método de referencia (14,27). Con respecto al factor de virulencia PVL, diversos estudios han mostrado que la presencia de este gen está asociada con un gran aumento en la severidad de la enfermedad (3,28-30), de ahí la necesidad de detectar esta toxina de manera a adoptar todas las medidas necesarias para evitar su transmisión y diseminación. Se han reportado diferentes métodos de detección de la toxina de PVL, y la detección por PCR es una forma rápida y práctica de realizar (19,31-33).
Con nuestros aislados obtuvimos 100% de concordancia entre el método fenotípico y molecular en la detección de la meticilino resistencia, sin embargo, grupos de investigación de Dinamarca y Reino Unido han reportado en el año 2011, nuevos homólogos del gen mecA, que presentan diferencias en la secuencia de ADN y que no son detectables por métodos moleculares descritos con anterioridad (34,35). Guillén y col. (36), en nuestro país, encontraron 2 aislados de S. aureus portadores de una variante del gen mecA que no genera producto de PCR utilizando los cebadores descritos por Murakami y col. (18), sin embargo si puede ser detectado empleando los oligonucleótidos degenerados descritos por García-Álvarez y col. (35), en junio del año 2011, poniendo de manifiesto la variabilidad genética de las cepas de S. aureus circulantes en nuestro país. Por este motivo sería importante analizar la presencia de un homólogo del gen mecA en aquellos casos en que no se observe concordancia, o buscar otros mecanismos de resistencia como la hiperproducción de batalactamasa o la alteración de otras PBPs(35,37,38).
Por otro lado, esta técnica también fue utilizada en la caracterización de aislados de ECN de muestras clínicas en las que se obtuvo 100% de correlación entre la detección del gen mecA por PCR y el método comercial de aglutinación que detecta la PBP2a, sin embargo con el método de difusión utilizando discos de cefoxitina se obtuvo un resultado discordante, se detectó la presencia del gen mecA en un aislado meticilino sensible por el método de difusión (39). Varios estudios muestran muy buena sensibilidad y especificidad entre los métodos fenotípicos y moleculares en la detección de la meticilino resistencia con S. aureus, sin embargo para ECN se han reportado disminución en la exactitud de los métodos fenotípicos en comparación con la detección de gen mecA por PCR (37,40).
La técnica de PCR múltiple descrita en este trabajo es una herramienta útil en la confirmación de aislados de Estafilococos meticilino resistentes y en la identificación del gen pvl.Representa una herramienta útil para ayudar en la identificación temprana de cepas de SAMR-AC, en donde la identificación rápida y precisa es un paso importante para controlar la diseminación; además es una técnica relativamente sencilla capaz de detectar ambos genes en una sola reacción y puede ser aplicada a cualquier laboratorio de biología molecular.
Agradecimientos
A la Dra. Graciela Russomando, jefa del departamento de Biología Molecular y Genética del IICS, por su apoyo para la realización del trabajo en el laboratorio a su cargo.
Al Dr. Gabriel Gutkind de la cátedra de Microbiología de la Facultad de Farmacia y Bioquímica de la Universidad de Buenos Aires, Argentina, quien cedió gentilmente un aislado utilizado como control positivo para los genes mecA y pvl.
Este trabajo fue realizado como parte del trabajo de tesis del Curso de Maestría en Ciencias Biomédicas, IICS-UNA.
Fuentes de financiación: este trabajo recibió apoyo económico del Instituto de Investigaciones en Ciencias de la Salud- Universidad Nacional de Asunción-Paraguay y del CONACYT (Consejo Nacional de Ciencias y Tecnología).
REFERENCIAS BIBLIOGRAFICAS
1. Velázquez-Meza ME. Surgimiento y diseminación de Staphylococcus aureus meticilinorresistente. Salud Publica Méx 2005;47(5):381-7. [ Links ]
2. Ardanuy C, Cercenado E, Morosi M, Torres C. Detección Fenotípica de Mecanismos de Resistencia en Grampositivos. Procedimientos en Microbiología Clínica. Recomendaciones de la Sociedad Española de Enfermedades Infecciosas y Microbiología Clínica. Madrid : La Sociedad; 2011. [ Links ]
3. Kilic A, Li H, Stratton CW, Tang Y. Antimicrobial susceptibility patterns and staphylococcal cassette chromosome mec types of, as well as Panton-Valentine leukocidin occurrence among, methicillin-resistant Staphylococcus aureus isolates from children and adults in middle Tennessee. J Clin Microbiol 2006; 44(12):4436-40. [ Links ]
4. Gardam MA. Is methicillin-resistant Staphylococcus aureus an emerging community pathogen? A review of the literature. Can J Infect Dis 2000; 11(4):202-211. [ Links ]
5. Köck R, Becker K, Cookson B, van Gemert-Pijnen JE, Harbarth S, Kluytmans J, et al. Methicillin-resistant Staphylococcus aureus (MRSA): burden of disease and control challenges in Europe. Euro Surveill 2010;15(41):19688. [ Links ]
6. Gardella N, Picaso R, Predari SC, Lasala M, Foccoli M, Benchetrit GB, et al. Methicillin-resistant Staphylococcus aureus strains in Buenos Aires Teaching Hospitals: replacement of the multidrug resistant South American clone by another susceptible to rifampin, minocycline and trimethoprim-sulfamethoxazole. Rev Argent Microbiol 2005;37:156-60. [ Links ]
7. Sola C, Saka HA, Vindel A, Bocco JL. Córdoba Staphylococcus aureus Collaborative Study Group. High frecuency of Panton-Valentine leukocidin genes in invasive methicillin-susceptible Staphylococcus aureus strains and the relationship with methicillin-resistant Staphylococcus aureus in Córdoba Argentina. Eur J Clin Microbiol Infect Dis 2007; 26:281-6. [ Links ]
8. Malachowa N, DeLeo FR. Mobile genetic elements of Staphylococcus aureus. Cell Mol Life Sci 2010; 67(18):3057-71. [ Links ]
9. SCCmec. SCCmec English Home Page (Internet). USA: Department of Bacteriology, School of Medicine, Juntendo University. (cited 3 de diciembre de 2010). Disponible en: http://www.staphylococcus.net/ [ Links ]
10. Gordon RJ, Lowy FD. Pathogenesis of methicillin-resistant Staphylococcus aureus infection. Clin Infect Dis 2008 Jun 1;46 (Suppl 5):S350-9. [ Links ]
11. Boyle-Vavra S, Daum RS. Community-acquired methicillin-resistant Staphylococcus aureus: the role of Panton-Valentine leukocidin. Lab Invest. 2006 Dic 4;87(1):3-9. [ Links ]
12. Soloaga R, Corso A, Gagetti P, Faccone D, Galas M. Detección de meticilino-resistencia en Staphylococcus aureus: Comparación de métodos convencionales y aglutinación con MRSA-Screen latex. Rev Argent Microbiol 2004;36(1):36-40. [ Links ]
13. Clinical and Laboratory Standards Institute (CLSI). Performance Standards for Antimicrobial Susceptibility testing; nineteenth informational supplement. CLSI 2009, Ene;29(3):M02-7. [ Links ]
14. OPS. Informe anual de la Red de Monitoreo/Vigilancia de la Resistencia a los Antibióticos. 2008. (monografia en Internet). Washington: OPS-USAID; 2008. (citado 3 de diciembre 2010). Disponible en: http://www.lachealthsys.org/index.php. [ Links ]
15. Winn WN, Allen SD, Janda WM, Koneman EW, Procop GW, et al. Koneman-Diagnóstico microbiológico: texto y atlas en color. 6º ed. Buenos Aires: Médica Panamericana; 2008. [ Links ]
16. De Paulis AN, Predari SC, Chazarreta CD, Santoianni JE. Five test simple scheme for species level identification of clinical significant coagulase-negative staphylococci. J Clin Microbiol 2003; 41:1219-24. [ Links ]
17. Zhang K, Sparling J, Chow BL, Elsayed S, Hussain Z, Church DL, et al. New quadriplex PCR assay for detection of methicillin and mupirocin resistance and simultaneous discrimination of Staphylococcus aureus from coagulase-negative staphylococci. J Clin Microbiol 2004 Nov; 42(11):4947-55. [ Links ]
18. Murakami K, Minamide W, Wada K, Nakamura E, Teraoka H, Watanabe S. Identification of methicillin-resistant strains of staphylococci by polymerase chain reaction. J Clin Microbiol 1991 Oct; 29(10):2240-44. [ Links ]
19. Lina G, Piémont Y, Godail-Gamot F, Bes M, Peter MO, Gauduchon V, et al. Involvement of Panton-Valentine leukocidin-producing Staphylococcus aureus in primary skin infections and pneumonia. Clin Infect Dis 1999 Nov; 29(5):1128-32. [ Links ]
20. Kolman S, Arielly H, Paitan Y. Evaluation of a Single and double-locu real-time PCR assays for methicillin-resistant Staphylococcus aureus (MRSA) surveillance. BMC Res Notes (revista en Internet) 2010 (citado 10 de noviembre de 2011); 3:110. Disponible en: http://www.biomedcentral.com/1756-0500/3/110. [ Links ]
21. DeBuyser ML, Morvan A, Grimont F, ElSolh N. Characterization of Staphylococcus Species by Ribosomal RNA Gene Restriction Patterns. J Gen Microbiol 1989 Apr;135(4):989-99. [ Links ]
22. Oliveira D, DeLancastre H. Multiplex PCR Strategy for Rapid Identification of Structural Types and Variants of the mec Element in Methicillin-Resistant Staphylococcus aureus.Antimicrob Agents Chemother 2002; 46(7):2155-61. [ Links ]
23. Pérez-Roth E, Claverie-Martín F, Villar J, Méndez-Alvarez S. Multiplex PCR for Simultaneous Identification of Staphylococcus aureus and Detection of Methicillin and Mupirocin Resistance. J Clin Microbiol 2001 39(11): 4037-41. [ Links ]
24. McClure J, Conly JM, Lau V, Elsayed S, Louie T, Hutchins W, et al. Novel multiplex PCR assay for detection of the staphylococcal virulence marker Panton-Valentine leukocidin genes and simultaneous discrimination of methicillin-susceptible from -resistant staphylococci. J Clin Microbiol 2006 Mar;44(3):1141-4. [ Links ]
25. Brakstad OG, Aasbakk K, Maeland JA. Detection of Staphylococcus aureus by polymerase chain reaction amplification of the nuc gene. J Clin Microbiol 1992 30:1654-60. [ Links ]
26. Shopsin B, Gomez M, Waddington M, Riehman M, Kreiswirth BN. Use of coagulase gene (coa) repeat region nucleotide sequences for typing of methicillin-resistant Staphylococcus aureus strains. J Clin Microbiol 2000 38:3453-6. [ Links ]
27. Mimica MJ, Berezin EN, Carvalho RLB, Mimica IM, Mimica LMJ, Sáfadi MAP, et al. Detection of methicillin resistance in Staphylococcus aureus isolated from pediatric patients: is the cefoxitin disk diffusion test accurate enough? Braz J Infect Dis 2007 Ago;11(4):415-7. [ Links ]
28. Al-Talib H, Hasan H, Yean C, Al-Ashwal SN, Ravichandran M. Fatal Necrotizing Pneumonia Caused by Panton-Valentine Leucocidin-Producing Hospital-Acquired Staphylococcus aureus: a Case Report Jpn. J Infect Dis 2011 64(1):58-60. [ Links ]
29. Brady JM, Stemper ME, Weigel A, Chyou P, Reed KD, Shukla SK. Sporadic "transitional" community-associated methicillin-resistant Staphylococcus aureus strains from health care facilities in the United States. J Clin Microbiol 2007 Ago;45(8):2654-61. [ Links ]
30. Palombarani S, Gardella N, Tuduri A, Figueroa S, Sly G, Corazza R, et al. Community-acquired methicillin-resistant Staphylococcus aureus infections in a hospital for acute diseases. Rev Argent Microbiol 2007 Sep;39(3):151-5. [ Links ]
31. Gauduchon V, Werner S, Prévost G, Monteil H, Colin DA. Flow Cytometric Determination of Panton-Valentine Leucocidin S Component Binding. Infect Immun 2001; 69(4): 2390-5. [ Links ]
32. Blanco R, Ezpeleta G, Cisterna R. Rapid real-time SYBRGreen assay for Panton Valentine leukocidin detection in staphylococcal infections. Scheveningen, Netherlands: 5th European Meeting on Molecular Diagnostics; 2007. [ Links ]
33. Badiou C, Dumitrescu O, George N, Forbes ARN, Drougka E, Chan KS, et al. Rapid Detection of Staphylococcus aureus Panton-Valentine Leukocidin in Clinical Specimens by Enzyme-Linked Immunosorbent Assay and Immunochromatographic Tests. J Clin Microbiol 2010 Abr 1;48(4):1384-90. [ Links ]
34. Shore AC, Deasy EC, Slickers P, Brennan G, O'Connell B, Monecke S, et al. Detection of Staphylococcal Cassette Chromosome mec Type XI Carrying Highly Divergent mecA, mecI, mecR1, blaZ, and ccr Genes in Human Clinical Isolates of Clonal Complex 130 Methicillin-Resistant Staphylococcus aureus. Antimicrob Agents Chemother 2011 Ago;55(8):3765-73. [ Links ]
35. García-Álvarez L, Holden MT, Lindsay H, Webb CR, Brown DF, Curran MD, et al. Meticillin-resistant Staphylococcus aureus with a novel mecA homologue in human and bovine populations in the UK and Denmark: a descriptive study. Lancet Infect Dis (revista en Internet) 2011 (citado 10 de Julio de 2011); 11(8):595-603. Disponible en: http://www.thelancet.com/journals/laninf/article/PIIS1473-3099%2811%2970126-8/fulltext1473-3099%2811%2970126-8/fulltext. [ Links ]
36. Guillén R, Basualdo W, Castro H, Campuzano A, Macchi M, Ortellado J, et al. Staphylococcus aureus adquiridos en la comunidad: Caracterización clínica, fenotípica y genotípica de aislados en niños que concurren a hospitales de referencia de Asunción y Dpto. central. Resumen 167. Rev Inst Med Trop 2011 Nov;6(supl):44. [ Links ]
37. Kaiser T, Pacheco F, Avelino A, Pereira E, Netto K, Ferreira A. Avaliação de métodos comumente usados em laboratórios para a determinação da suscetibilidade à oxacilina entre amostras de Staphylococcus sp, isoladas de um hospital de Vitória, Estado do Espírito Santo. Rev. Soc. Bras. Med. Trop 2010;43(3):298-303. [ Links ]
38. Batista N, Gutierrez I, Lara M, Laich F, Méndez S. Evaluación del método de difusión en disco de 30µg de cefoxitina en la detección de resistencia a meticilina en aislamientos seleccionados de Staphylococcus aureus. Rev Esp Quimioter 2008;21(4):213-6. [ Links ]
39. Fariña N, Carpinelli L, Samudio M, Guillén R, Laspina F, Sanabria R, et al. Estafilococos Coagulasa Negativos Clínicamente Significativos. Especies más frecuentes y Factores de Virulencia. Resumen 091. Rev Inst Med Trop 2011 Nov;6(supl):28. [ Links ]
40. Souza A, Secchi C, Reiter K, Rodrigues L, Peixoto A, Alves P. Evaluation of oxacillin and cefoxitin disks for detection of resistance in coagulase negative staphylococci. Mem Inst Oswaldo Cruz 2007; 102(6):719-23. [ Links ]
*Autor Correspondiente: Dra.(PhD) Rosa María Guillén Fretes, Dpto. de Biología Molecular y Genética, Instituto de Investigaciones en Ciencias de la Salud-Universidad Nacional de Asunción.
Email microbiologia@iics.una.py.
Fecha de recepción:marzo de 2012, Fecha de aceptación: mayo 2012