INTRODUCCION
La sepsis es un síndrome caracterizado por anormalidades fisiológicas, patológicas y bioquímicas que se producen como respuesta a una infección1-3. Es una condición que genera alta morbilidad y mortalidad en donde la detección temprana de los microorganismos causantes es esencial para un manejo oportuno.
El diagnóstico rápido del agente causal de las bacteriemias, ha constituido un reto continuo para la microbiología y la medicina, las cuales buscan un tratamiento antimicrobiano dirigido en beneficio de la vida del paciente4,5.
Los hemocultivos siguen siendo el Gold estándar para el diagnóstico de las Infecciones del torrente sanguíneo en niños6 ya que confirma el diagnóstico de bacteriemia, el cual requiere aislamiento de patógenos para identificación definitiva y susceptibilidad antimicrobiano. Este proceso puede durar hasta 72 horas o más, lo que causa retraso en el diagnóstico6,7.
Actualmente se han desarrollado una variedad de técnicas moleculares para la detección de patógenos8 como la Reacción en cadena polimerasa multiplex en tiempo real para sepsis; Este método fue diseñado para la detección de 24 patógenos y 3 genes de resistencia a antibióticos asociados con infecciones del torrente sanguíneo; Con sólo una prueba se puede identificar patógenos en 9 de cada 10 hemocultivos positivos, lo cual permiten tipificar de forma rápida los microorganismos y dar así un manejo dirigido7,8.
El objetivo del presente estudio fue determinar la frecuencia de detección y tipificación de los microorganismos por el PCR multiplex (Film Array) en pacientes pediátricos (menores de 18 años) ingresados al servicio de urgencias con el diagnóstico confirmado de sepsis por hemocultivo.
MATERIALES Y METODOS
Se realizó un estudio observacional descriptivo retrospectivo, de corte transversal. Se revisaron los paneles de sepsis PCR multiplex (Film Array) de pacientes pediátricos ingresados en el servicio de urgencias y terapia intensiva pediátrica, de la fundación Infantil Club Noel de Cali con sospecha de sepsis, en el periodo comprendido entre diciembre 01 del 2016 a marzo 31 del 2019 y cuyos resultados fueron positivos tanto el panel molecular como los hemocultivos.
Se excluyeron los reportes que carecían de datos demográficos del paciente.
Se comparó los resultados del hemocultivo con el del Film Array. Se determinó la prueba simultánea de bacterias, virus, levaduras, parásitos y genes resistentes a los antimicrobianos. El panel detecta 24 patógenos, y 3 genes de resistencia mecA- resistencia a Meticilina; vana/B - resistencia a Vancomicina y KPC - resistencia a carbapenémicos de los patógenos contenidos en la muestra de hemocultivos positivos
Las variables estudiadas fueron edad, sexo, procedencia, diagnósticos principales, tipo de gérmenes aislados, antibioticoterapia y la mortalidad.
Técnica del PCR multiplex (Film Array): es un sistema de amplificación, detección y análisis del material genérico de una variedad de microorganismos con certificación de la Food and Drug Administration (FDA), cuya técnica es rápida y los resultados pueden estar disponible entre 1 y 2 horas.
El presente trabajo fue presentado y aprobado por el comité de ética institucional, respetando los principios de ética de la investigación.
El análisis de los datos se realizó con el programa Excel 2016. La edad se presenta en porcentajes de grupos etarios y mediana con rangos intercuartílicos Las variables cualitativas en porcentajes.
RESULTADOS
Se revisaron 111 paneles positivos para sepsis de pacientes pediátricos pediátricos menores de 18 años, que ingresaron durante el periodo de estudio. Se excluyeron 10 del estudio porque presentaban datos demográficos incompletos.
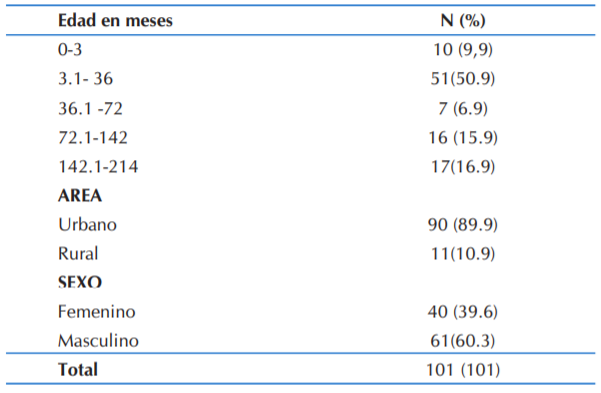
La edad mediana de los pacientes fue de 26 meses (IQR 11 - 95,5 meses) Otros datos demográficos de los pacientes incluidos se encuentran en la Tabla 1.
En la tabla 2 se observan las patologías de los pacientes participantes
Tabla 2 características clínicas y paraclínicas de los pacientes atendidos en hospital infantil club Noel

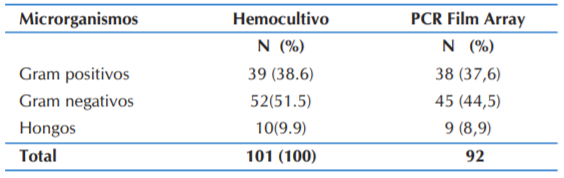
La comparación de los resultados del hemocultivo con el Panel Film Array se encuentra en la tabla 3.
La tipificación de los gérmenes se observa en la Tabla 4
DISCUSIÓN
En el presente estudio el panel molecular detecto en un porcentaje similar a los encontrado en otros reportes, entre 90 a 100% dependiendo de la capacidad del Film Array9-11. La capacidad de tener los resultados de los gérmenes responsables de las infecciones en poco tiempo con el panel molecular Film Array en relación al hemocultivo, permite tomar decisiones terapéuticas tempranas y con un target microbiano definido12,13.
En cuanto a los microrganismos aislados correspondieron a bacterias de predominio gram negativos en comparación a gram positivos y hongos, siendo este hallazgo esperable puesto que estas constituyen la mayor etiología de la sepsis y bacteriemia en la población pediátrica sobre todo en los lactantes que representan la mayor población de nuestro estudio. También se podría relacionar a condiciones médicas asociados, comorbilidades y factores de riesgo asociados teniendo en cuenta que el estudio se hizo tanto de pacientes de urgencia y unidad de cuidado intensivo pediátrico en donde el uso de catéteres, la estancia prolongada, la resistencia antibiótica que representa factores de riesgo para la invasión de bacterias gram negativas; Esto refleja la importancia de este método en el diagnóstico oportuno para las enterobacterias las cuales representan altas tasas de mortalidad 11,13,14.
En cuanto a enterobacterias más comunes se encontró a klebsiella pneumonie en mayor porcentaje que los observados en otros estudios como el realizado por la Universidad de jordán donde solo se presentó en el 7.4 % en población ligeramente diferente a la del presente estudio, en el que se incluyó a lactantes en mayor proporción y la patología respiratoria fue predominante frente a la gastrointestinal del citado estudio15.
Entre las bacterias Gram positivas cabe resaltar como streptococo pneumonie solo se presentó en proporción menor al stafilococcus aureus. Estos resultados son diferentes a lo reportado en otro estudio en el que encontraron una prevalencia entre el 30 y el 50% como responsable de neumonías y bacteriemia16
La fungemia se observó en escaso porcentaje en el presente estudio. La mayoría fueron detectados con el Fillm Array. Otros estudios como el realizado por Pauloci et al, encontró una capacidad de detección del 91 %17. Es muy importante la capacidad de detección de este método en fungemia asociado a coinfecciones, teniendo en cuenta que los métodos diagnósticos para fungemia no son altamente sensibles ni tienen buen rendimiento diagnóstico18.
Algo de destacar en este estudio la importancia de este método a la hora de tomar una decisión sobre cobertura antibiótica. Un tratamiento antibiótico dirigido y oportuno puede ayudar a disminuir la resistencia microbiana.
Los casos con hemocultivo positivos en los que no hubo detección por la nueva tecnología fillm array, podría deberse a alteración en la cantidad y calidad de la muestra y/o las características metabólicas de los diferentes microorganismos
La mortalidad en el presente estudio fue baja.
En cuanto a las limitaciones, al ser una nueva tecnología diagnóstica, lleva poco tiempo de implementación. El escaso número de muestras no permite generalizar los resultados a otras poblaciones.